
Les voies de signalisation cellulaire sont des réseaux moléculaires complexes qui permettent aux cellules de détecter et de répondre aux signaux provenant de leur environnement ou de leur état interne. Ces voies transmettent l’information depuis les récepteurs membranaires vers des effecteurs intracellulaires grâce à l’activation séquentielle de protéines de signalisation telles que les kinases, les protéines adaptatrices et les facteurs de transcription.
À travers ces cascades de signalisation, les cellules coordonnent des fonctions biologiques essentielles, notamment la prolifération, la différenciation, le métabolisme, les réponses immunitaires et l’adaptation aux stress environnementaux.
La dérégulation des voies de signalisation est fréquemment associée à de nombreuses pathologies majeures, telles que les cancers, les maladies auto-immunes, les troubles métaboliques ou les maladies neurodégénératives.
Chez AnyGenes®, nous aidons les chercheurs à surmonter les défis liés à l’analyse de réseaux de signalisation complexes. Nos plus de 1000 panels SignArrays® prêts à l’emploi, basés sur la technologie qPCR, offrent des résultats rapides, fiables et reproductibles. Compatibles avec des échantillons standards ou précieux (FFPE, LCM), nos arrays permettent d’accélérer les découvertes et de réaliser un profilage précis des voies de signalisation.
Découverez nos SignArrays® et lancez dès aujourd’hui votre analyse de voies de signalisation.
L’étude des voies de signalisation repose sur la mesure des changements moléculaires qui reflètent l’activation d’une voie biologique. Une stratégie largement utilisée consiste à analyser les réponses transcriptionnelles déclenchées par les cascades de signalisation.
Lorsqu’une voie de signalisation est activée, des facteurs de transcription régulent l’expression de gènes cibles impliqués dans la réponse cellulaire. Le suivi de ces signatures transcriptionnelles permet aux chercheurs de caractériser l’activité des voies de signalisation et d’étudier les mécanismes biologiques associés à certaines pathologies ou à des conditions de stress cellulaire.
L’analyse ciblée de l’expression génique à l’aide de qPCR arrays dédiés aux voies de signalisation constitue une approche robuste pour quantifier les variations transcriptionnelles coordonnées entre plusieurs composants d’une voie et leurs gènes cibles
Parmi les voies de signalisation les plus étudiées figurent notamment :
Chacune de ces voies peut être étudiée à l’aide de l’analyse de l’expression génique ciblée grâce aux SignArrays® AnyGenes®.
Les voies de signalisation cellulaire peuvent être classées selon les processus biologiques qu’elles régulent. Ces réseaux moléculaires coordonnent la communication cellulaire et contrôlent des fonctions essentielles telles que la prolifération, le métabolisme, l’inflammation ou la survie cellulaire.
Les principales catégories de voies de signalisation comprennent :
Ces voies régulent le métabolisme cellulaire et l’équilibre énergétique.
Exemples :
Ces voies sont largement étudiées dans les maladies métaboliques, l’obésité et le diabète.
Ces voies sont activées en réponse au stress cellulaire, aux infections ou aux dommages tissulaires.
Exemples :
Elles jouent un rôle central dans l’inflammation, les réponses immunitaires et la progression tumorale.
Ces voies contrôlent les décisions de destin cellulaire et le développement des tissus.
Exemples :
La dérégulation de ces voies est souvent associée à des troubles du développement et à différents cancers.
Certaines voies sont directement impliquées dans des processus pathologiques spécifiques, notamment :
La compréhension de ces voies de signalisation permet aux chercheurs d’identifier de nouveaux biomarqueurs et cibles thérapeutiques.
Nos SignArrays® sont utilisés mondialement et cités dans des publications scientifiques.
Profitez de :
Cliquez sur l’image ci-dessous pour sélectionner votre panel de voies de signalisation préféré.
Toutes nos SignArrays® sont validées expérimentalement sur un large panel de tissus et lignées cellulaires grâce à notre plateforme moléculaire à haut débit. Un contrôle qualité strict garantit des résultats fiables et reproductibles, renforçant la confiance dans vos données.
Chaque plaque 96 puits permet d’analyser 84 gènes d’intérêt, avec 8 gènes de référence pour une normalisation robuste et 4 contrôles qualité. Pour les études plus larges, les plaques 384 puits peuvent couvrir plusieurs voies simultanément.
Disponibles pour de nombreuses espèces : Homo sapiens, Mus musculus, Rattus norvegicus, Sus scrofa, et plus sur demande
Nos arrays prennent en charge des études sur des processus biologiques clés tels que :
Nous proposons également des options de personnalisation flexibles, pour sélectionner les gènes et voies les plus pertinents à votre projet
Personnalisez vos SignArrays® avec les facteurs de votre choix !
Téléchargez simplement notre fichier d’information
et envoyez-le à
[email protected]
pour démarrer votre projet.


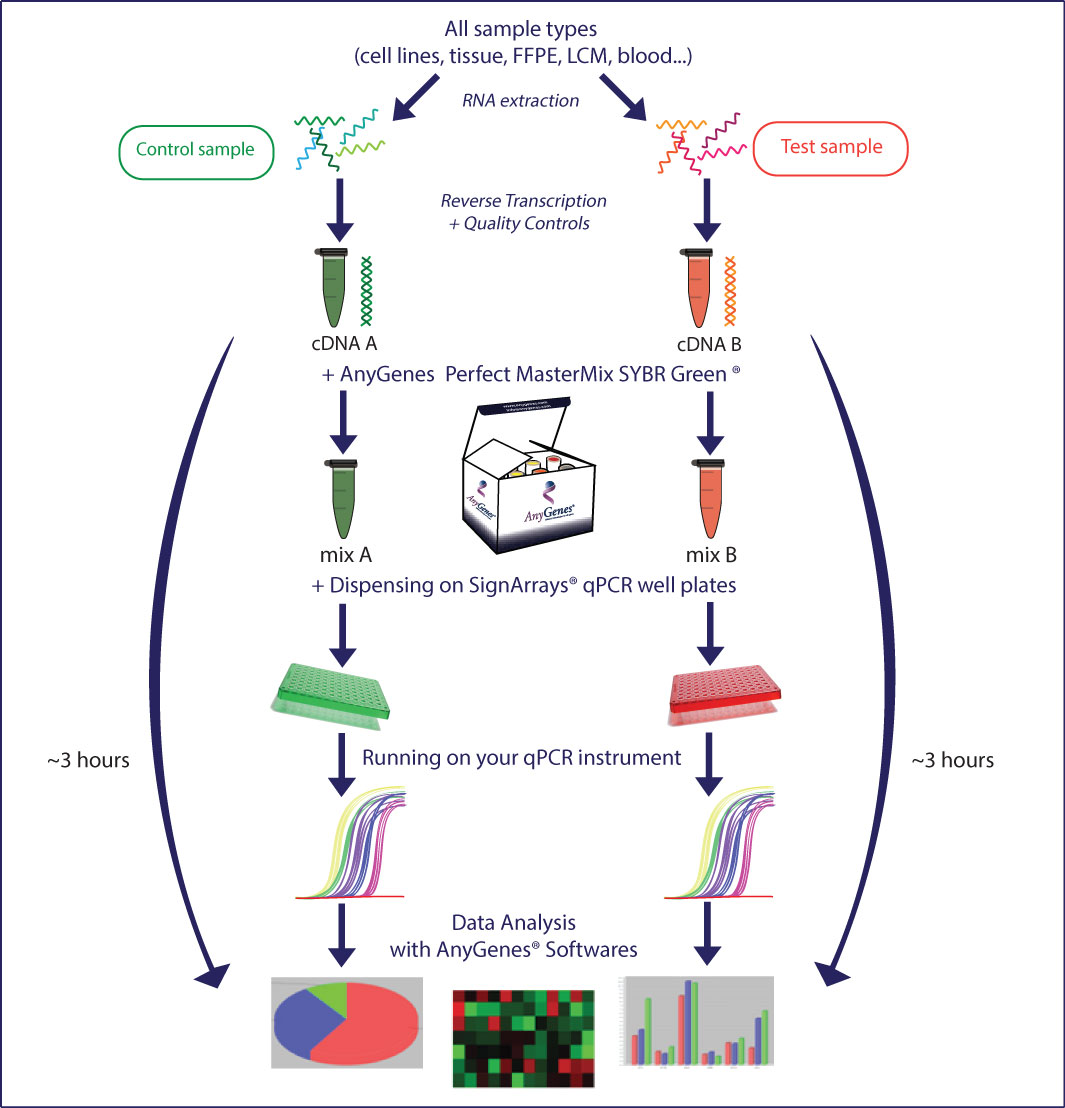
Les résultats de votre analyse de voies de signalisation SignArrays® en moins de 2 heures ! AnyGenes a mis au point et standardisé ses protocoles SignArrays® pour vous laisser réaliser très facilement vos analyses qPCR.
Les voies de signalisations SignArrays® sont des outils parfaits pour de nombreuses applications :
Voie de signalisation spécifique (plaques 96 ou 384 puits)
+ Réactifs de qPCR hautement sensibles et robustes
(Perfect Master Mix SYBR® Green & EvaGreen)
+ Outil d’analyse de données libre d’accès
+ Compatible avec tous les appareils de qPCR

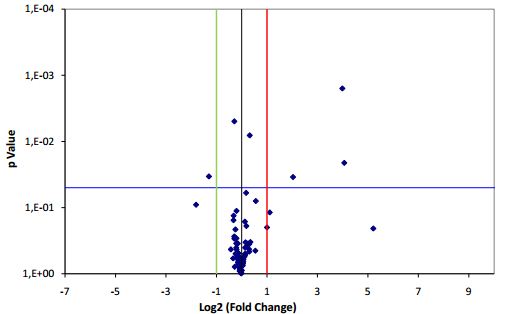

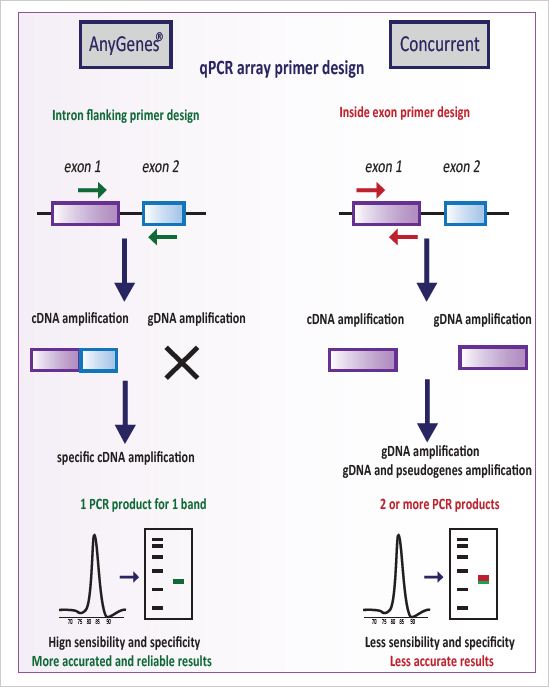
– Afin de garantir des résultats sensibles, spécifiques et robustes, le design de chaque lot de primers est réalisé avec des critères hautement stringents, puis ceux-ci validés au niveau expérimental sur une large collection de tissus et lignées cellulaires sur notre plateforme moléculaire haut débit par le biais de contrôles qualité stricts.
– Nous vous offrons par ce biais des primers de très haute qualité.
– Avec un design de primers sur 2 exons (si possible, selon les gènes d’intérêts) pour garantir une spécificité optimale en qPCR et éviter toute amplification d’ADNg pouvant éventuellement contaminer l’échantillon.


Vous avez d’autres applications en tête à développer en fonction de vos projets ? Contactez nous à [email protected]

Les SignArrays® AnyGenes® servent à relier la recherche fondamentale aux études cliniques : validation de biomarqueurs, analyse d’échantillons patients et étude des processus biologiques clés tels que l’inflammation, la signalisation du cancer et la réponse au stress cellulaire.
Pour la liste complète des publications utilisant nos SignArrays®, consultez notre bibliographie.
Angiogenesis, the formation of blood vessels, occurs in a coordinated series of steps, which can be divided into a destabilization, a proliferation, and a maturation phase.
Extensive studies have revealed a variety factors involved in neoangiogenesis, the main protagonists are: Vascular endothelial Growth Factor (VEGF), basic Fibroblast Growth Factor (bFGF), various members of the Transforming Growth factor beta (TGFβ) family and hypoxia (Hypoxia-inducible transcription factor, HIF)… Other factors that have angiogenic properties include the angiopoietins, (Ang-1); hepatocyte growth factor (HGF); Platelet-derived growth factor (PDGF-BB); Insulin-like growth factor family (IGF-1, IGF-2) and the Neurotrophins (NGF).
One of earliest events in angiogenesis is the degradation of the vascular basement membrane and the remodeling of the extracellular matrix (ECM). Several matrix metalloproteinases (MMPs), including MMP-2, -3, and -9 play an important role in this system, and are associated with tumor progression, including invasion, metastasis, growth, migration, and angiogenesis.
Integrins are the principle adhesion receptors used by endothelial cells to interact with the extracellular environment and are necessary for cell migration, proliferation, and survival.
Apoptosis or programmed cell death is a highly regulated process critical for normal development and tissue homeostasis. Aberrant regulation of apoptosis can lead to cancer. Apoptosis is induced from signals inside or outside the cell including radiation, viral infection, growth factors, and hormones. Apoptosis involves signature morphological changes induced by caspases, which are activated upon induction of apoptotic signalling and cleave downstream molecules to facilitate the apoptotic cascade. The induction of apoptosis can occur through two pathways: the intrinsic apoptotic pathway which involves signalling through the mitochondria and the extrinsic apoptotic pathway which is initiated through activation of cell surface death receptors. Apoptotic signalling through the intrinsic pathway primarily involves activation of the proapoptotic Bcl-2 family members Bax and Bak, which facilitate release of cytochome C from the mitochondria and subsequent caspase-9 cleavage or activation. The activated caspase-9 will finally cleave or activate the downstream effector caspases such as caspase-3 and -7, leading to apoptosis.This pathway is negatively regulated by several antiapoptotic Bcl-2 family members such as Bcl-2 and Bcl-XL. Apoptotic signalling through the extrinsic pathway is initiated by ligand binding to death receptors or by induction of trimerization of the receptors. The death receptors belong to the tumor necrosis factor (TNF) receptor superfamily, which includes Fas, TNFR1, DR3, DR4 (TRAIL-R1),DR5(TRAIL-R2),and DR6.
Autophagy is a lysosomal catabolic process that leads to sequestration and degradation of intracellular material. It functions at basal level in every cell and contributes to maintain cellular homeostasis, clearance of damaged organelles and adaptation to environmental stresses.
In contrast, if the autophagy activity is too high, it may promote Apoptosis.
Autophagy is involved in preventing certain types of disease: however dysfunction of autophagy has been implicated in multiple human diseases including cancer, neurodegeneration, and pathogen infection.
Analyses of molecular mechanism have provided huge advances toward understanding the molecular basis of autophagy. The signaling pathways that are involved in mammalian autophagy imply specific genes or proteins called Atg, in particular Atg5 which exhibits a dual function by modelling both autophagy and apoptosis like Bcl-2. It is also well known that mTOR (target of rapamycin) an evolutionarily-conserved protein kinase, plays a crucial role as a regulator of autophagy.
As AnyGenes® policy is to propose you complete solutions at the closest of your scientific issues, you can custom your own SignArrays® with the genes of interest of your choice, according to your project.
You just have to download and complete our Personalized SignArrays® information file and send it at [email protected]
Oui, nos arrays sont validés pour les échantillons précieux et limités tels que FFPE ou LCM.
84 gènes par plaque 96 puits ; plusieurs voies possibles avec les plaques 384 puits.
Tous les instruments qPCR standards sont compatibles.
Oui, nos SignArrays® couvrent les voies liées au cancer, aux maladies auto-immunes, neurodégénératives, cardiovasculaires et autres pathologies.
Télécharger le fichier d’informations SignArrays® personnalisés, sélectionnez vos gènes d’intérêt et envoyez-le à [email protected] pour commencer vos projets.
Vous cherchez plus d’informations ? Visitez notre section Aide & FAQ pour découvrir tous les détails sur nos produits, services et support technique.
Prix pour le système SignArrays® 96 Standard
| Reference type : XXX1H1-Y* | |
| Standard | |
| Number of SignArrays® 96 | Price/unit (before TAX) |
|---|---|
* Y: R, A, B or F plate type, according to the qPCR instrument
Prix pour le système SignArrays® 96 personnalisable
Reference type : PZXH1-Y* | |
| Personnalisable | |
| Number of SignArrays® 96 | Price/unit (before TAX) |
|---|---|
* Y: R, A, B or F plate type, according to the qPCR instrument
Prix des réacifs PMS associés avec SignArrays® 96
| Reference type : PMS1-Z* |
|
| PMS Perfect Master Mix SYBR® Green SignArrays® 96* | |
| Number of SignArrays® 96 |
Price/unit (before TAX) |
|---|---|
* 10 μl of PMS/reaction for 20 μl final volume
* Z: W, R, LR or F PMS, according to the qPCR instrument
Prix pour le système SignArrays® 384 Standard
| Reference type : XXX1H2-Y* | |
| Standard | |
| Number of SignArrays® 384 | Price/unit (before TAX) |
|---|---|
* Y: R, A, B or F plate type, according to the qPCR instrument (cf Compatibility file)
Prix pour le système SignArrays® 384 personnalisable
| Reference type : PZXH2-Y* | |
| Personnalisable | |
| Number of SignArrays® 384 | Price/unit (before TAX) |
|---|---|
* Y: R, A, B or F plate type, according to the qPCR instrument (cf Compatibility file)
Prix des réactifs PMS associés avec SignArrays® 384
| Reference type : PMS2-Z* |
|
| PMS (Perfect Master Mix SYBR® Green) SignArrays® 384* | |
| Number of SignArrays® 384 |
Price/unit (before TAX) |
|---|---|
* 5 μl of PMS/reaction for 10 μl final volume
* Z: W, R, LR or F PMS, according to the qPCR instrument (cf Compatibility file)
|
Signaling Pathways
Average Star Rating is 4.8/5 from the Total 450 Ratings
|
